Neue Einblicke in die erste Pestpandemie durch alte Genome
Die Analyse von acht neu rekonstruierten Pestgenomen der ersten historisch überlieferten Pestpandemie offenbart eine bisher unbekannte Diversität und erbringt erstmals den genetischen Nachweis der Justinianischen Pest auf den Britischen Inseln.
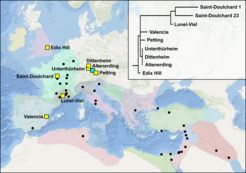
Im Jahr 541 begann die „Justinianische Pest“, benannt nach dem damals regierenden Kaiser Justinian I., im Byzantinischen Reich, in der Folge suchte für nahezu 200 Jahre eine verheerende Seuche in mehreren Wellen Europa und den Mittelmeerraum heim. Zeitzeugen hinterließen Berichte über das Ausmaß der Pandemie, die Schätzungen zufolge bis zu 25% der Bevölkerung des Römischen Reichs ausgelöscht hat. Genetische Studien konnten in den letzten Jahren nachweisen, dass das Bakterium Yersinia pestis für die Pandemie verantwortlich war. Die Wege der Ausbreitung der Pest und die Verwandtschaft der Pest-Erreger der zahlreichen Ausbrüche während der ersten Pandemie untereinander waren bislang unbekannt.
In der neuen Studie analysierte ein internationales Forschungsteam unter Leitung des Jenaer Max-Planck-Instituts für Menschheitsgeschichte menschliche Überreste aus Mehrfachbestattungen von 21 archäologischen Fundorten in Österreich, Großbritannien, Deutschland, Frankreich und Spanien. Das Team konnte acht neue Y.-pestis-Genome rekonstruieren, die einen Vergleich mit bereits publizierten alten und modernen Pestgenomen erlaubten. Außerdem gelang dem Team der bislang früheste genetische Nachweis der Pest in Großbritannien an Proben aus Edix Hill, einem Gräberfeld aus der Zeit der Angelsachsen. Durch die Kombination von archäologischen Datierungen und die Position des Pestgenoms im evolutionären Stammbaum gelang es, den Schluss zu ziehen dass dieses Genom mit einer nicht eindeutig beschriebenen Seuche in Zusammenhang steht, die für die Britischen Inseln im Jahr 544 überliefert ist.
Große Vielfalt von Y.-pestis-Stämmen während der ersten Pandemie
Die im Rahmen der Studie neu rekonstruierten Genome aus Großbritannien, Frankreich, Deutschland und Spanien offenbaren eine bislang unbekannte Diversität von Peststämmen im Europa des 6. bis 8. Jahrhunderts. „Die Rekonstruktion dieser Genome aus geographisch wie zeitlich so unterschiedlichen Zusammenhängen erlaubt uns, die Mikrodiversität des Pesterregers in Europa während der ersten Pandemie zu untersuchen“, erklärt Ko-Erstautor Marcel Keller, Doktorand am Max-Planck-Institut für Menschheitsgeschichte und derzeit tätig an der Universität Tartu. Die neuen Genome zeigen, dass mehrere eng verwandte Y.-pestis-Stämme während der 200 Jahre dauernden Pandemie in Europa zirkulierten, manche vermutlich sogar zeitgleich in derselben Region.

Obwohl nun deutlich mehr Genome dieser Epoche vorliegen, konnte die Frage nach dem Ursprung der Justinianischen Pest nicht geklärt werden. Keller erklärt: „Der Stamm entwickelte sich vermutlich einige hundert Jahre vor der ersten Pandemie in Zentralasien, aber unsere Daten erlauben uns momentan noch keine Rückschlüsse auf den Ursprung der Justinianischen Pest, vor den ersten überlieferten Ausbrüchen 541 in Ägypten. Allerdings deutet die Tatsache, dass die Genome alle eine gemeinsame Abstammungslinie haben, darauf hin, dass sich die Pest in Europa oder dem Mittelmeerraum festsetzen konnte und nicht mehrmals eingetragen wurde.“
Möglicher Hinweis für konvergente Evolution während zweier unabhängiger historischer Pandemien
Ein weiteres interessantes Ergebnis der Studie ist, dass die Genome der späten ersten Pandemie einen kleinen Teil des Genoms verloren haben, auf dem sich auch zwei Virulenzfaktoren befanden, die vermutlich zur Gefährlichkeit des Pesterregers beitrugen. Ein ähnlicher Verlust (Deletion) an Erbmaterial findet sich auch in späten Genomen der Zweiten Pandemie, etwa 800 bis 1000 Jahre später. „Das ist möglicherweise ein Fall von konvergenter Evolution. Das heißt, dass sich diese Peststämme zwar unter ähnlichen Umständen, aber unabhängig voneinander zweimal in gleicher Weise entwickelt haben. Die Mutation könnte eine Anpassung an eine besondere ökologische Nische in Westeurasien darstellen, wo die Pest während beider Pandemien zirkulierte“, erklärt Ko-Erstautorin Maria A. Spyrou vom Max Planck Institut für Menschheitsgeschichte.

Lunel-Viel (Languedoc-Südfrankreich). Pestopfer, das in den Ausbruchgraben eines gallorömischen Hauses geworfen wurde. Ende 6./Anfang 7. Jahrhundert.
Die genetischen Befunde ergänzen die historischen, archäologischen und paläoepidemiologischen Zeugnisse der ersten historisch überlieferten Pestpandemie und helfen somit offene Fragen zu beantworten. „Diese Studie zeigt das Potenzial der Paläogenetik für das Verständnis historischer und moderner Pandemien durch den Vergleich von Genomen über Jahrtausende hinweg“, erklärt der Studienleiter Johannes Krause, Direktor am Max-Planck-Institut für Menschheitsgeschichte. „Durch umfangreichere Beprobungen möglicher Pestgräber hoffen wir einen Beitrag zum Verständnis der Mikroevolution von Y. pestis während vergangener und gegenwärtiger Pandemien und deren Auswirkungen auf den Menschen zu leisten.“


