Neue Methode zur Identifizierung alter DNA
Die neu entwickelte Software PyDamage ermöglicht die automatisierte Abschätzung der Beschädigungen alter DNA und die Authentifizierung von De-novo-DNA-Assemblagen
De-novo-DNA-Assemblierung ist eine Methode zur Rekonstruktion von Genomen aus einer großen Menge von DNA-Fragmenten, deren ursprüngliche Herkunft unbekannt ist. Die Methode wird zunehmend eingesetzt, um zum Beispiel aus Fäkalien und Zahnstein von archäologischen Stätten genomische Daten zu gewinnen und mit deren Hilfe, die Vielfalt und Funktionalität vergangener Mikrobiome zu untersuchen.
Aussagekräftige Ergebnisse lassen sich dabei nur erzielen, wenn es gelingt, bei der Analyse alte DNA von modernen DNA-Einträgen zu unterscheiden. Die Tools, die es derzeit zur Identifizierung alter DNA gibt, sind jedoch darauf ausgelegt, Schäden innerhalb der DNA einer einzelnen bekannten Referenzsequenz zu finden, wie z. B. dem menschlichen Genom, aber nicht für die riesige Zahl von Sequenzen aus mehreren unbekannten Quellen, die für die De-novo-DNA-Assemblierung typisch sind.
Um dieses Problem zu lösen, hat ein Forschungsteam unter Leitung des Jenaer Max-Planck-Instituts für Menschheitsgeschichte PyDamage, eine Software zur automatisierten und parallelen Abschätzung von Schäden an De-novo-Zusammensetzungen alter DNA und zur Aut und zur Authentifizierung von de novo-Zusammensetzungen alter DNA entwickelt.
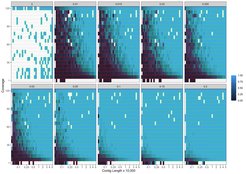
Um schnell Schadensmuster für zahlreiche Referenzsequenzen parallel abzuschätzen, nutzt die Software eine Likelihood-Ratio, so dass die Wissenschaftler/-innen ein Profil der Schäden innerhalb eines DNA-Segments erstellen können. Mit anderen Worten, die Software führt eine statistische Abschätzung der Wahrscheinlichkeit durch, dass eine DNA-Sequenz kontaminiert ist. Dadurch kann zwischen wirklich alten DNA-Abschnitten und DNA-Abschnitten, die von modernen Verunreinigungen stammen, unterschieden werden.
In einer aktuellen Studie testete das Forschungsteam PyDamage sowohl an simulierten als auch an empirischen DNA-Daten von archäologischen Fäkalien und zeigte die Fähigkeit der Software, zuverlässig und automatisch DNA-Segmente zu identifizieren, die für alte DNA charakteristische Schäden aufweisen.
PyDamage war erwartungsgemäß am zuverlässigsten bei der Vorhersage von Schäden für DNA-Segmente mit höherer Abdeckung, größerer Länge und schwereren Schäden und bietet vor allem einen statistischen Rahmen für die Bewertung von Schäden, welcher Forschenden beim Studiendesign und bei der Sequenzierungsplanung hilft.
"Die De-novo-Assemblierung von alter DNA bleibt eine Herausforderung, aber jetzt haben wir ein Werkzeug, das uns sagt, ob das, was wir assembliert haben, wahrscheinlich alt ist", sagt Maxime Borry, einer der Autoren der Studie.
Da sich die Bereiche Mikrobiologie und Evolutionsbiologie zunehmend den archäologischen Aufzeichnungen zuwenden, um die dynamische Evolutionsgeschichte mikrobieller Gemeinschaften zu untersuchen, sind Werkzeuge, die zuverlässig alte metagenomische DNA assemblieren und authentifizieren, von entscheidender Bedeutung für das Verständnis der mikrobiellen Gemeinschaften um und in uns. Gekoppelt mit der De-novo-Assemblierung alter DNA öffnet PyDamage neue Türen, um die funktionelle Vielfalt alter Metagenome zu erforschen und zu verstehen.
